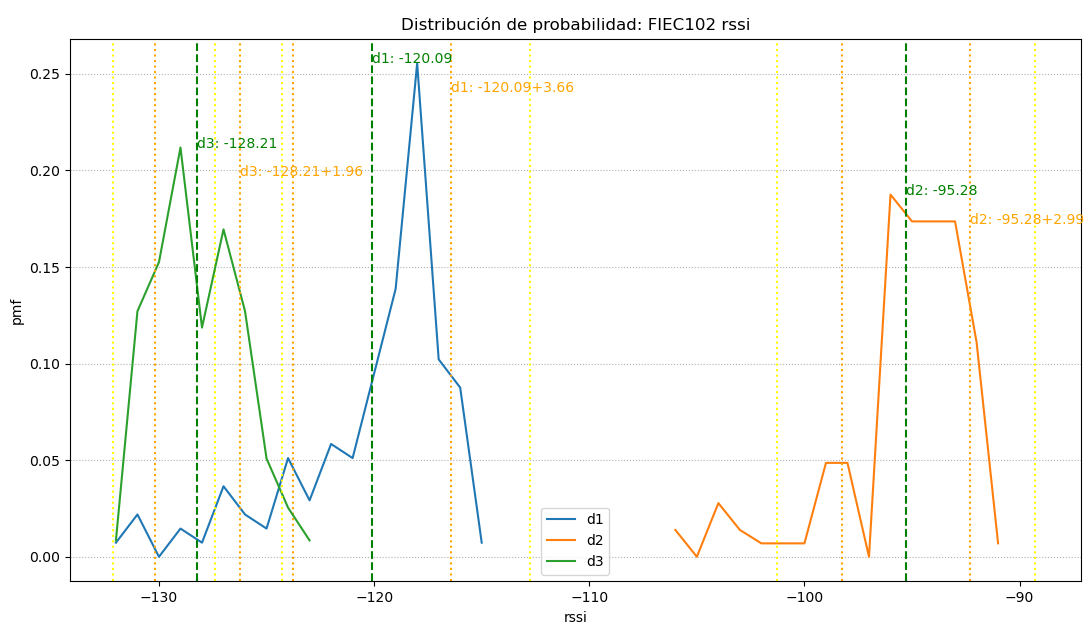
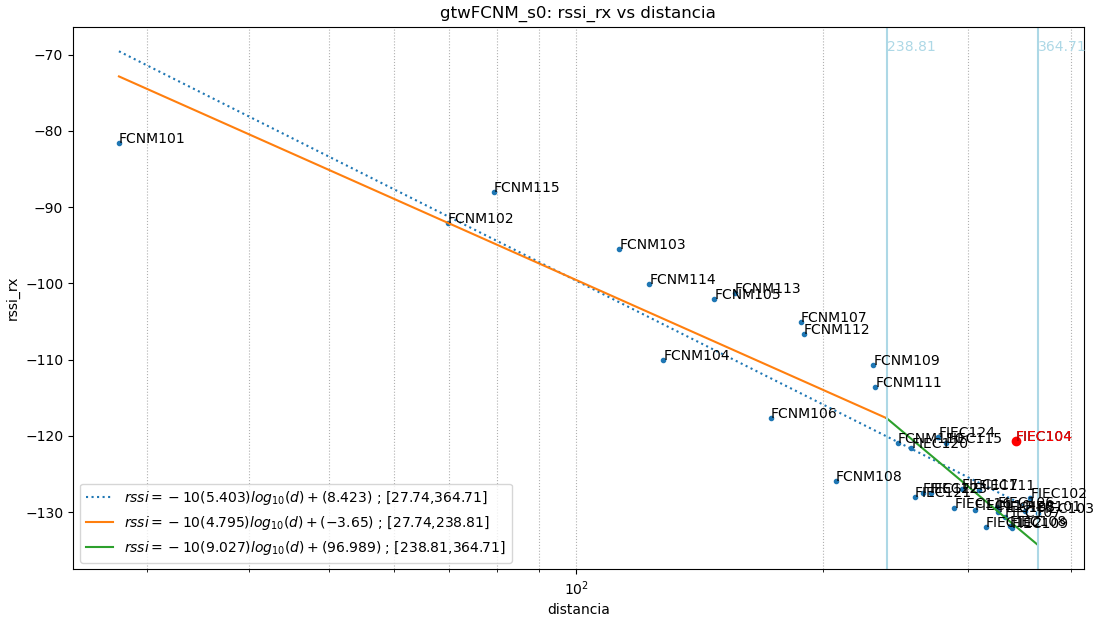
El efecto «sombra» añade el parámetro sector a la ecuación que se incorpora al resultado de la linealización en cada baliza.
La ecuación de una baliza se compone entonces de dos parámetros de selección: sector e intervalo. 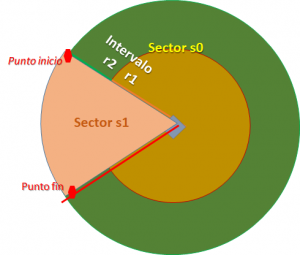
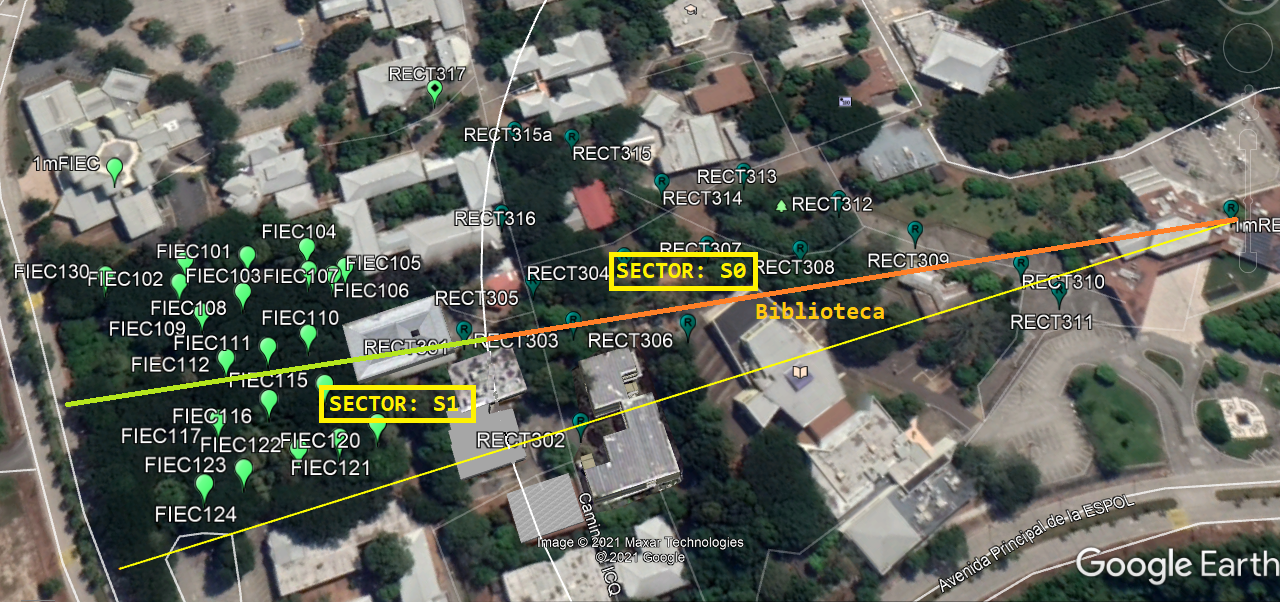
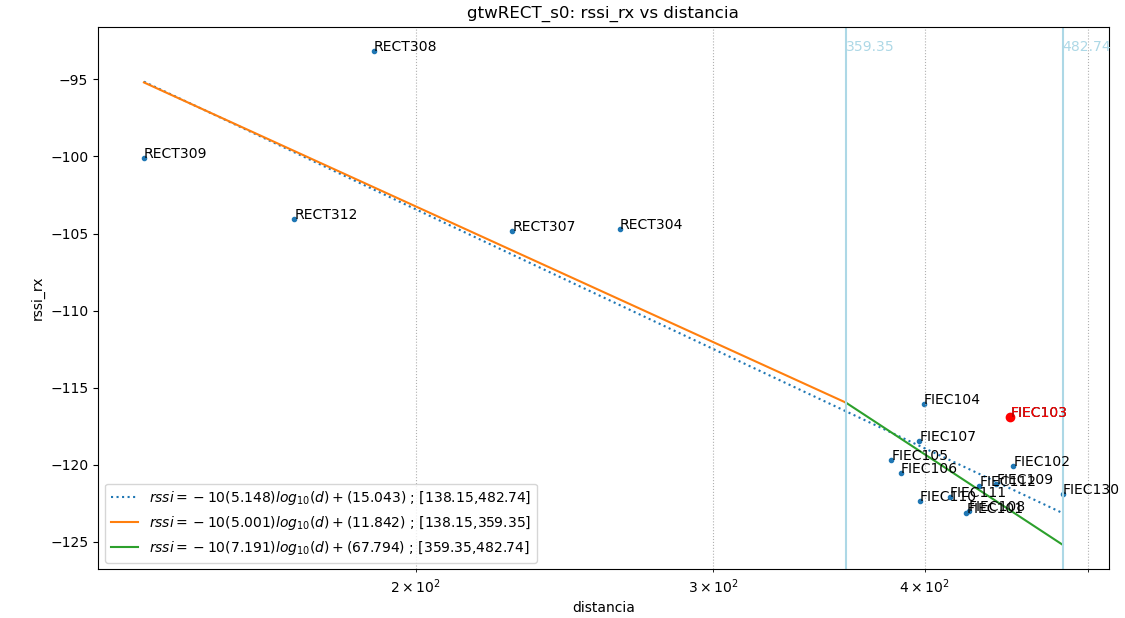
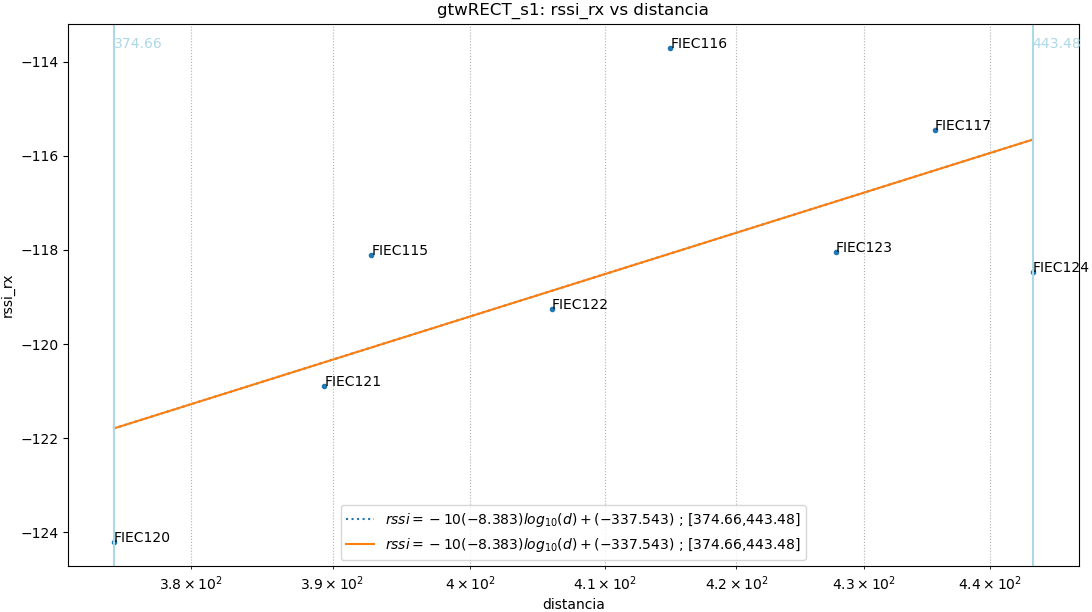
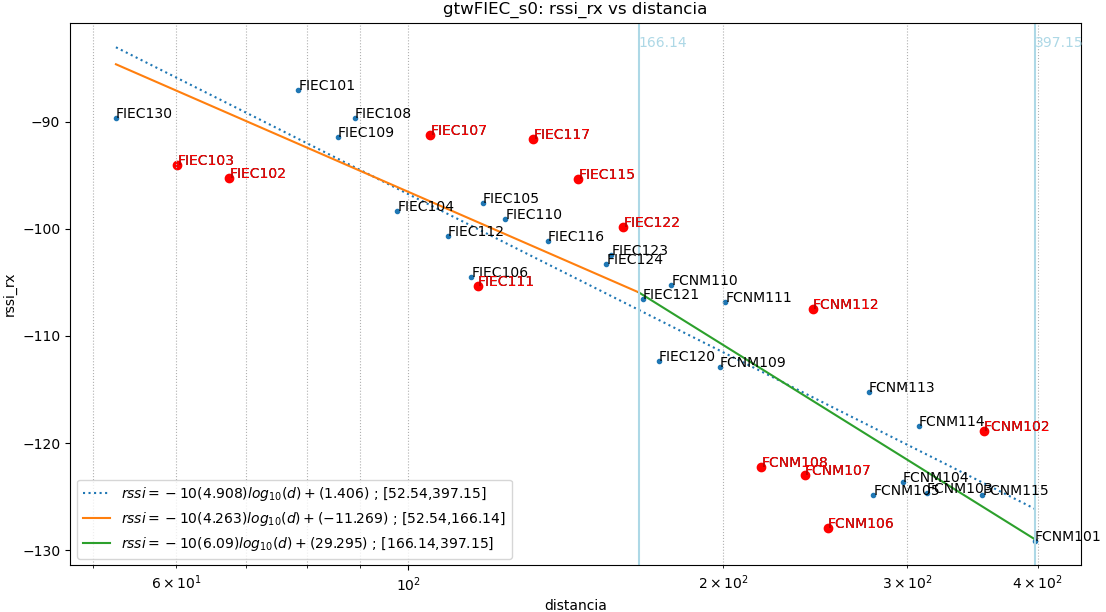
Como ilustración se muestra la figura que tiene tres partes o ecuaciones:
ecuacion[‘s0’][‘r1’]
ecuacion[‘s0’][‘r2’]
ecuacion[‘s1’][‘r0’]
El primer parámetro para seleccionar la ecuación es el sector, ‘s0’ y ‘s1’, que en caso que sea un solo círculo se identifica como ‘s0’.
Dentro de cada sector, se mantiene el concepto de intervalos de distancia o radio. Se mantiene el concepto de la sección anterior, donde ‘r0’ corresponde a la linealización de todos los puntos en el sector. Cuando exiten sub-intervalos se usa ‘r1’, ‘r2’, etc para cada intervalo.
El número de ecuaciones corresponde al número de balizas y sectores establecidos para el análisis.
Se realizan cambios menores a la función pares_usar() de la librería girni para incorporar el parámetro sector, que al ser vacío '' funciona como fué descrito en las secciones anteriores.
pares_usar(tabla,baliza, analiza,unabaliza, unsector =», medida = ‘rssi’, modo = ‘rx’)
También se actualizaron los nombres de los archivos de entrada y salida para diferenciar de los resultados anteriores y disponer de los archivos para comparar con los resultados del método que solo usa intervalos.
Algoritmo en Python
# LoRa-Multipunto, Rssi vs distancia con mínimos cuadrados
# linealización Rssi vs log10(distancia)
# por Sectores e intervalos , Graficas '2D'
# Girni 2020-10-07 propuesta: edelros@espol.edu.ec
import numpy as np
import pandas as pd
import json
import matplotlib.pyplot as plt
import girni_lora_libreria as girni
# INGRESO
# archivos de entrada
modo = 'rx'
medida = 'rssi'
arch_medidaubica = 'rsmP06_'+medida+'Ubica01sector1.txt'
# archivos de salida
arch_ecuaciones = 'rsmP07_ecuacionSector01.json'
arch_medUbAtrib = 'rsmP07_'+medida+'UbicaUsarSector01.txt'
# Analizar por segmentos
analiza = {'gtwRECT':{'analizar' : 1,
'sector_ref' : ['FIEC112','FCNM110'],
's0':{'atipico_std' : 1,
'frontera' : [300],
'atipInterv_std': [2,2],
'p_amplia': 2,
'grp' : ['RECT','FIEC'],
'tip' : ['punto'],
'LOS' : [1] },
's1':{'atipico_std' : 1,
'frontera' : [],
'atipInterv_std': [2],
'p_amplia': 2,
'grp' : ['FIEC','FCNM'],
'tip' : ['punto'],
'LOS' : [1,0] }
},
'gtwFIEC':{'analizar' : 1,
'sector_ref' : [],
's0':{'atipico_std' : 1,
'frontera' : [190],
'atipInterv_std': [1,1],
'p_amplia': 4,
'grp' : ['FIEC','FCNM'],
'tip' : ['punto'],
'LOS' : [0,1] }
},
'gtwFCNM':{'analizar' : 1,
'sector_ref' : [],
's0':{'atipico_std' : 1,
'frontera' : [235.0],
'atipInterv_std': [2,2],
'p_amplia': 4,
'grp' : ['FIEC','FCNM'],
'tip' : ['punto'],
'LOS' : [1,0] }
}
}
baliza = {'d1':'gtwRECT',
'd2':'gtwFIEC',
'd3':'gtwFCNM'}
# Parámetros de grafica
tipograf = '2D' # '2D','' sin grafica
escala = 'log' # 'normal','log'
escalabase = 10 # 10
casicero = 1e-4
precision = 2
intersectar = 1 # 0:Falso, 1: Verdadero
# PROCEDIMIENTO
# leer datos
tabla = pd.read_csv(arch_medidaubica, index_col='etiqueta')
tabla = pd.DataFrame(tabla)
baliza_key = list(baliza.keys())
baliza_val = list(baliza.values())
# Resultados de análisis
ecuacion = {}
eq_graf = {}
# analiza datos hacia una baliza
for unabaliza in analiza:
donde = baliza_val.index(unabaliza)
cualbaliza = baliza_key[donde]
# Parámetros
analizar = analiza[unabaliza]['analizar']
if analizar:
# Crea ecuacion por baliza
ecuacion[unabaliza] = {'sector_rad':[]}
eq_graf[unabaliza] = {}
# sectores
sectores = []
sector_ref = analiza[unabaliza]['sector_ref']
tabla['sector_'+cualbaliza] = 0 # 'todos' predeterminado
# coordenadas baliza para identificar ángulo
b_este = tabla['c_este'][unabaliza]
b_norte = tabla['c_norte'][unabaliza]
# sectores por puntos de referencia
if len(sector_ref)>0:
for cadapunto in sector_ref:
p_este = tabla['c_este'][cadapunto]
p_norte = tabla['c_norte'][cadapunto]
dx = p_este - b_este
dy = p_norte - b_norte
theta = np.arctan2(dy,dx)
if theta<0 and dx<0:
theta = theta + 2*np.pi
sectores.append(theta)
sectores = np.array(sectores)
ordenar = np.argsort(sectores)
sectores = list(sectores[ordenar])
nsectores = len(sectores)
# clasifica puntos por sector particular
for cadapunto in tabla.index:
dentrosector = 0
p_este = tabla['c_este'][cadapunto]
p_norte = tabla['c_norte'][cadapunto]
dx = p_este-b_este
dy = p_norte-b_norte
theta = np.arctan2(dy,dx)
if theta<0 and dx<0:
theta = theta + 2*np.pi
for j in range(0,nsectores-1,1):
if theta>sectores[j] and theta<sectores[j+1]:
dentrosector = j+1
tabla.loc[cadapunto,'sector_'+cualbaliza] = dentrosector
# ecuacion por baliza y sector
ecuacion[unabaliza]['sector_rad'] = sectores
nsectores = len(sectores)
if nsectores == 0:
nsectores = 1
for cadasector in range(0,nsectores,1):
unsector = 's'+str(cadasector)
ecuacion[unabaliza][unsector] = {}
eq_graf[unabaliza][unsector] = {}
# ecuación con todos los puntos como referencia
[pares,par_etiqueta] = girni.pares_usar(tabla,baliza,analiza,
unabaliza,unsector,
medida,modo)
xi = pares[:,0]
yi = pares[:,1]
n_xi = len(xi)
# coeficiente de correlación
correlacion = np.corrcoef(xi,yi)[0,1]
# minimos cuadrados
ecuacion0 = girni.linealiza_lstsq(xi,yi)
# selecciona atipicos de todos los puntos
atipico_std = analiza[unabaliza][unsector]['atipico_std']
alpha = ecuacion0['alpha']
beta = ecuacion0['beta']
fdist0 = lambda d: -10*alpha*(np.log10(d))+beta
yi0 = fdist0(xi)
dyi0std = ecuacion0['error_std']
dyi0 = yi - yi0
atipicos = np.abs(dyi0) >= dyi0std*atipico_std
xi0_e = xi[atipicos]
yi0_e = yi[atipicos]
etiq0_e = par_etiqueta[atipicos]
unintervalo = 'r0' # todos
# para exportar hacia archivo o gráfica
ecuacion[unabaliza][unsector] = {unintervalo: ecuacion0 }
ecuacion[unabaliza][unsector][unintervalo]['correlacion'] = correlacion
eq_graf[unabaliza][unsector] = {unintervalo: {'xi_graf' : xi,
'yi_graf' : yi,
'etiqueta' : par_etiqueta,
'linea' : yi0,
'atipicos' : [xi0_e,yi0_e],
'atip_etiq': etiq0_e}
}
# Intervalos radiales en sector
intervalo = [np.min(xi),np.max(xi)]
frontera = analiza[unabaliza][unsector]['frontera']
if len(frontera)>0:
# revisar si frontera esta dentro intervalo
frontera = np.array(frontera, dtype=float)
revisar = (frontera>=np.min(xi)) & (frontera<=np.max(xi))
enintervalo = list(frontera[revisar])
intervalo.extend(enintervalo)
intervalo = np.array(intervalo)
ordenar = np.argsort(intervalo)
intervalo = intervalo[ordenar]
n_intervalo = len(intervalo)
# analizar cada subintervalo
p_inicio = 0
p_desde = 0
p_amplia = analiza[unabaliza][unsector]['p_amplia']
atipIntv_std = analiza[unabaliza][unsector]['atipInterv_std']
for i in range(0,n_intervalo-1,1):
i_eq = 'r' + str(i+1)
# puntos en subintervalo [a,b]
a = intervalo[i]
b = intervalo[i+1]
subintervalo = (xi >= a) & (xi <= b)
xi_sub = xi[subintervalo]
yi_sub = yi[subintervalo]
n_sub = len(xi_sub)
etiq_sub = par_etiqueta[p_inicio:p_inicio + n_sub]
# amplia sub-intervalo, mejora intersecta rectas
detras = p_inicio
retrocede = detras
if detras > p_amplia:
retrocede = p_amplia
delante = n_xi - (p_inicio+n_sub)# -1)
avanza = delante
if delante >= p_amplia:
avanza = p_amplia
p_desde = p_inicio - retrocede
p_hasta = p_inicio + (n_sub) + avanza
p_inicio = p_inicio + (n_sub-1)
# subintervalo, amplia puntos
xi_a = xi[p_desde:p_hasta]
yi_a = yi[p_desde:p_hasta]
etiq_a = par_etiqueta[p_desde:p_hasta]
# coeficiente de correlación
correlacion1 = np.corrcoef(xi_a,yi_a)[0,1]
# analiza subintervalo
ecuacion1 = girni.linealiza_lstsq(xi_a,yi_a)
ecuacion[unabaliza][unsector][i_eq] = ecuacion1
ecuacion[unabaliza][unsector][i_eq]['correlacion'] = correlacion1
# atipicos del subintervalo extendido
alpha = ecuacion1['alpha']
beta = ecuacion1['beta']
fdist1 = lambda d: -10*alpha*(np.log10(d))+beta
yi1 = fdist1(xi_a)
dyi1std = ecuacion1['error_std']
atipicos = np.zeros(len(xi_a),dtype=bool)
atipico_std = analiza[unabaliza][unsector]['atipInterv_std'][i]
dyi1 = yi_a - yi1
if np.abs(dyi1std) > casicero:
atipicos = np.abs(dyi1) >= dyi1std*atipico_std
xi1_e = xi_a[atipicos]
yi1_e = yi_a[atipicos]
etiq1_e = etiq_a[atipicos]
# para gráfica, atipicos sin extender puntos
atipicos_sub = (xi1_e >= a) & (xi1_e<=b)
xi_sub1_e = xi1_e[atipicos_sub]
yi_sub1_e = yi1_e[atipicos_sub]
etiq_sub1e = etiq1_e[atipicos_sub]
eq_graf[unabaliza][unsector][i_eq] = {'atipicos': [xi_sub1_e,yi_sub1_e],
'atip_etiq':etiq_sub1e}
# subintervalo sin atipicos
if len(xi1_e)>0:
atipicoNo = np.abs(dyi1) <= dyi1std*atipico_std
xi2 = xi_a[atipicoNo]
yi2 = yi_a[atipicoNo]
etiq2 = etiq_a[atipicoNo]
# coeficiente de correlación
correlacion2 = np.corrcoef(xi2,yi2)[0,1]
ecuacion2 = girni.linealiza_lstsq(xi2,yi2)
# actualiza ecuación sin atipicos intervaloy
intervalox = ecuacion1['intervalox']
ecuacion2['intervalox'] = intervalox.copy()
alpha = ecuacion2['alpha']
beta = ecuacion2['beta']
fdist = lambda d: -10*alpha*(np.log10(d))+beta
intervaloy = fdist(intervalox)
ordenar = np.argsort(intervaloy)
intervaloy = list(intervaloy[ordenar])
ecuacion2['intervaloy'] = intervaloy
ecuacion[unabaliza][unsector][i_eq] = ecuacion2
ecuacion[unabaliza][unsector][i_eq]['correlacion'] = correlacion2
# Revisar frontera entre subintervalos,
# calcula intersección de rectas como nueva frontera
interv_calc = np.copy(intervalo)
if len(intervalo) >2 and intersectar==1 :
for i in range(0,n_intervalo-2,1):
ai = 'r' + str(i+1)
bi = 'r' + str(i+2)
ma = ecuacion[unabaliza][unsector][ai]['alpha']
ba = ecuacion[unabaliza][unsector][ai]['beta']
mb = ecuacion[unabaliza][unsector][bi]['alpha']
bb = ecuacion[unabaliza][unsector][bi]['beta']
# punto de intersección o cruce
cruzanx = 10**((bb-ba)/(10*(mb-ma)))
dfrontera = frontera - cruzanx
# cruce dentro de intervalo de ecuacion
if cruzanx > intervalo[-1]:
cruzanx = intervalo[-1]
if cruzanx < intervalo[0]:
cruzanx = intervalo[0]
interv_calc[i+1] = cruzanx
# para grafica evalua cada subintervalo sin atipicos
n_interv_calc = len(interv_calc)
for i in range(0,n_interv_calc-1,1):
i_eq = 'r'+str(i+1)
a = interv_calc[i]
b = interv_calc[i+1]
subintervalo = (xi >= a) & (xi <= b)
xi_sub = xi[subintervalo]
yi_sub = yi[subintervalo]
xi_graf = np.copy(xi[subintervalo])
if not(a in xi_graf):
xi_graf = np.concatenate(([a],xi_graf),axis=0)
if not(b in xi_graf):
xi_graf = np.concatenate((xi_graf,[b]),axis=0)
# Evalua subintervalo con la ecuacion sin atipicos
alpha = ecuacion[unabaliza][unsector][i_eq]['alpha']
beta = ecuacion[unabaliza][unsector][i_eq]['beta']
fdist = lambda d: -10*alpha*(np.log10(d))+beta
yi1_sub = fdist(xi_sub)
yi_graf = fdist(xi_graf)
eq_graf[unabaliza][unsector][i_eq]['xi_graf'] = xi_graf
eq_graf[unabaliza][unsector][i_eq]['yi_graf'] = yi_graf
a = np.round(np.min([xi_graf]),precision)
b = np.round(np.max([xi_graf]),precision)
ecuacion[unabaliza][unsector][i_eq]['intervalox'] = [a,b]
ay = np.round(np.min([yi_graf]),precision)
by = np.round(np.max([yi_graf]),precision)
ecuacion[unabaliza][unsector][i_eq]['intervaloy'] = [ay,by]
# SALIDA
for unabaliza in ecuacion:
for unsector in ecuacion[unabaliza]:
if unsector == 'sector_rad':
print('baliza: ',unabaliza)
print(' sectores radianes: ',ecuacion[unabaliza]['sector_rad'])
if unsector != 'sector_rad':
for i_eq in ecuacion[unabaliza][unsector]:
unintervalo = ecuacion[unabaliza][unsector][i_eq]['intervalox']
unintervaloy = ecuacion[unabaliza][unsector][i_eq]['intervaloy']
error_medio = ecuacion[unabaliza][unsector][i_eq]['error_medio']
error_std = ecuacion[unabaliza][unsector][i_eq]['error_std']
eq_latex = ecuacion[unabaliza][unsector][i_eq]['eq_latex']
errorx_medio = ecuacion[unabaliza][unsector][i_eq]['errorx_medio']
errorx_std = ecuacion[unabaliza][unsector][i_eq]['errorx_std']
correlacion = ecuacion[unabaliza][unsector][i_eq]['correlacion']
print(' [sector][intervalo]: ',unsector,',',i_eq)
print(' ' + eq_latex)
print(' ','intervalox: ',np.round(unintervalo,precision))
print(' ','intervaloy: ',np.round(unintervaloy,precision))
print(' correlación: ',np.round(correlacion,precision))
print(' |error_rssi| promedio: ',np.round(error_medio,precision),
' , std:',np.round(error_std,precision))
print(' |error_dist| promedio: ',np.round(errorx_medio,precision),
' , std:',np.round(errorx_std,precision))
print()
# salida hacia archivo
with open(arch_ecuaciones, 'w') as outfile:
json.dump(ecuacion, outfile)
tabla.to_csv(arch_medUbAtrib)
# GRAFICA
# Referencias para gráfica
grupo = ['FIEC' ,'FCNM' ,'RECT','CIRC']
colores = ['green','orange','grey','magenta']
tipo = ['punto','1m' ,'gtw','dispositivo']
marcas = [ 'o','D' ,'D' ,'*' ]
if tipograf=='2D':
for unabaliza in ecuacion:
for unsector in ecuacion[unabaliza]:
if not(unsector=='sector_rad'):
figura,grafica = plt.subplots()
if escala == 'log':
grafica.set_xscale(escala,base=escalabase)
# todos los puntos
unintervalo = 'r0'
xi = eq_graf[unabaliza][unsector][unintervalo]['xi_graf']
yi = eq_graf[unabaliza][unsector][unintervalo]['yi_graf']
etiqueta = eq_graf[unabaliza][unsector][unintervalo]['etiqueta']
grafica.scatter(xi,yi,marker='.')
m = len(xi)
for i in range(0,m,1):
grafica.annotate(etiqueta[i],(xi[i],yi[i]))
# linealizado con todos los puntos
fdtxt = ecuacion[unabaliza][unsector][unintervalo]['eq_latex']
yi0 = eq_graf[unabaliza][unsector][unintervalo]['linea']
a = np.round(np.min([xi]),precision)
b = np.round(np.max([xi]),precision)
eq_texto = fdtxt +' ; ['+ str(a) +','+ str(b)+']'
grafica.plot(xi,yi0,label=eq_texto,linestyle='dotted')
# linealizado por subintervalo
eq_interv = list(ecuacion[unabaliza][unsector].keys())
eq_interv.pop(0)
n_intervalo = len(eq_interv)
for i_eq in eq_interv:
fdtxt = ecuacion[unabaliza][unsector][i_eq]['eq_latex']
grtxt = ecuacion[unabaliza][unsector][i_eq]['eqg_latex']
xi_graf = eq_graf[unabaliza][unsector][i_eq]['xi_graf']
yi_graf = eq_graf[unabaliza][unsector][i_eq]['yi_graf']
a = np.round(np.min([xi_graf]),precision)
b = np.round(np.max([xi_graf]),precision)
eq_texto = fdtxt+' ; ['+str(a)+','+str(b)+']'
grafica.plot(xi_graf,yi_graf, label=eq_texto)
# atipicos marcados en subintervalo
[xi1_e,yi1_e] = eq_graf[unabaliza][unsector][i_eq]['atipicos']
etiq1_e = eq_graf[unabaliza][unsector][i_eq]['atip_etiq']
grafica.scatter(xi1_e,yi1_e, color='red')
m = len(etiq1_e)
for i in range(0,m,1):
grafica.annotate(etiq1_e[i],
(xi1_e[i],yi1_e[i]),
color='red')
# lineas de frontera
grafica.axvline(a, color='lightblue')
valor_frontera = str(np.round(a,precision))
grafica.annotate(valor_frontera,
(a,np.max([yi,yi0])),
color='lightblue')
grafica.axvline(b, color='lightblue')
valor_frontera = str(np.round(b,precision))
grafica.annotate(valor_frontera,
(b,np.max([yi,yi0])),
color='lightblue')
# etiquetas y títulos
grafica.legend()
grafica.set_ylabel(medida+'_'+modo)
grafica.set_xlabel('distancia')
grafica.grid(True,linestyle='dotted',
axis='x', which='both')
untitulo = unabaliza+'_'+unsector+': '
untitulo = untitulo+medida+'_'+modo+' vs distancia'
grafica.set_title(untitulo)
plt.show()